Poner estrellas en ggplot barplots y boxplots-para indicar el nivel de significación (valor p)
Es común poner estrellas en gráficas de barras o gráficas de caja para mostrar el nivel de significación (valor p) de uno o entre dos grupos, a continuación se muestran varios ejemplos:
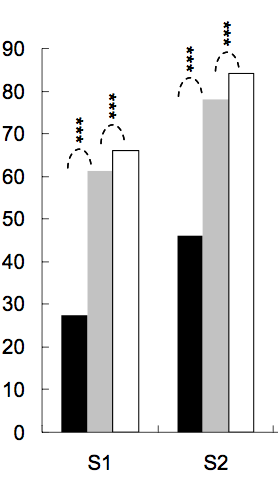
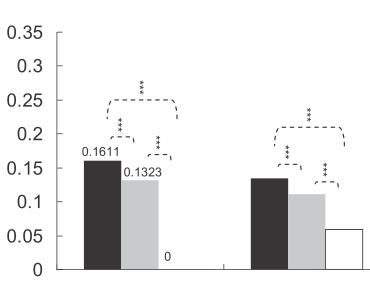
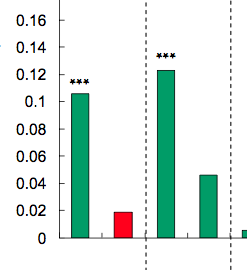
El número de estrellas se define por el valor p, por ejemplo, se puede poner 3 estrellas para el valor p
Y mis preguntas: ¿Cómo generar gráficos similares? Los métodos que automáticamente ponen estrellas basadas en el nivel de significación son más que bienvenidos.
4 answers
Por favor, encuentre mi intento a continuación.
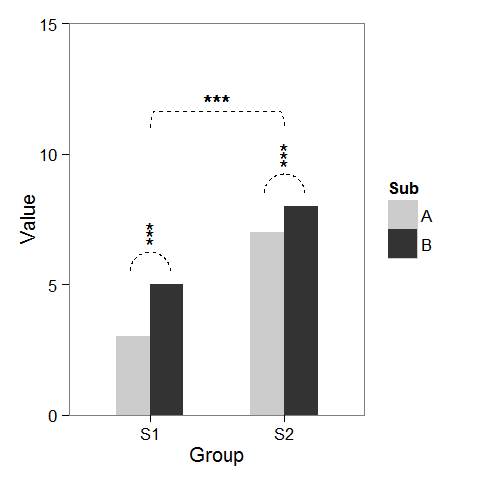
Primero, creé algunos datos ficticios y una gráfica de barras que se puede modificar como queramos.
windows(4,4)
dat <- data.frame(Group = c("S1", "S1", "S2", "S2"),
Sub = c("A", "B", "A", "B"),
Value = c(3,5,7,8))
## Define base plot
p <-
ggplot(dat, aes(Group, Value)) +
theme_bw() + theme(panel.grid = element_blank()) +
coord_cartesian(ylim = c(0, 15)) +
scale_fill_manual(values = c("grey80", "grey20")) +
geom_bar(aes(fill = Sub), stat="identity", position="dodge", width=.5)
Agregar asteriscos encima de una columna es fácil, como baptiste ya mencionó. Simplemente crea un data.frame con las coordenadas.
label.df <- data.frame(Group = c("S1", "S2"),
Value = c(6, 9))
p + geom_text(data = label.df, label = "***")
Para agregar los arcos que indican una comparación de subgrupos, calculé coordenadas paramétricas de un semicírculo y las agregué conectadas con geom_line. Los asteriscos necesitan nuevas coordenadas, demasiado.
label.df <- data.frame(Group = c(1,1,1, 2,2,2),
Value = c(6.5,6.8,7.1, 9.5,9.8,10.1))
# Define arc coordinates
r <- 0.15
t <- seq(0, 180, by = 1) * pi / 180
x <- r * cos(t)
y <- r*5 * sin(t)
arc.df <- data.frame(Group = x, Value = y)
p2 <-
p + geom_text(data = label.df, label = "*") +
geom_line(data = arc.df, aes(Group+1, Value+5.5), lty = 2) +
geom_line(data = arc.df, aes(Group+2, Value+8.5), lty = 2)
Por último, para indicar la comparación entre grupos, construí un círculo más grande y lo aplané en la parte superior.
r <- .5
x <- r * cos(t)
y <- r*4 * sin(t)
y[20:162] <- y[20] # Flattens the arc
arc.df <- data.frame(Group = x, Value = y)
p2 + geom_line(data = arc.df, aes(Group+1.5, Value+11), lty = 2) +
geom_text(x = 1.5, y = 12, label = "***")
Warning: date(): Invalid date.timezone value 'Europe/Kyiv', we selected the timezone 'UTC' for now. in /var/www/agent_stack/data/www/ajaxhispano.com/template/agent.layouts/content.php on line 61
2014-11-22 02:17:17
Sé que esta es una vieja pregunta y la respuesta de Jens Tierling ya proporciona una solución para el problema. Pero recientemente creé una extensión ggplot que simplifica todo el proceso de agregar barras de significado: ggsignif
En lugar de agregar tediosamente geom_line y geom_text a su parcela, simplemente agregue una sola capa geom_signif:
library(ggplot2)
library(ggsignif)
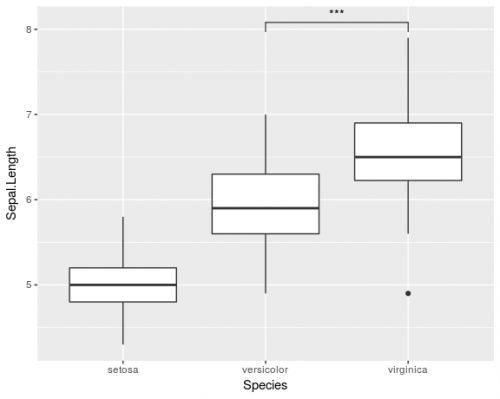
ggplot(iris, aes(x=Species, y=Sepal.Length)) +
geom_boxplot() +
geom_signif(comparisons = list(c("versicolor", "virginica")),
map_signif_level=TRUE)
Para crear un gráfico más avanzado similar al mostrado por Jens Tierling, puede do:
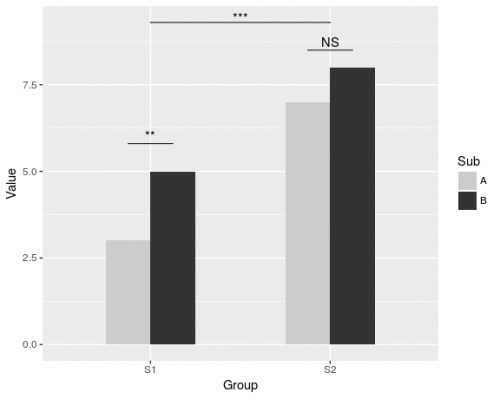
dat <- data.frame(Group = c("S1", "S1", "S2", "S2"),
Sub = c("A", "B", "A", "B"),
Value = c(3,5,7,8))
ggplot(dat, aes(Group, Value)) +
geom_bar(aes(fill = Sub), stat="identity", position="dodge", width=.5) +
geom_signif(stat="identity",
data=data.frame(x=c(0.875, 1.875), xend=c(1.125, 2.125),
y=c(5.8, 8.5), annotation=c("**", "NS")),
aes(x=x,xend=xend, y=y, yend=y, annotation=annotation)) +
geom_signif(comparisons=list(c("S1", "S2")), annotations="***",
y_position = 9.3, tip_length = 0, vjust=0.4) +
scale_fill_manual(values = c("grey80", "grey20"))
La documentación Completa del paquete está disponible en CRAN.
Warning: date(): Invalid date.timezone value 'Europe/Kyiv', we selected the timezone 'UTC' for now. in /var/www/agent_stack/data/www/ajaxhispano.com/template/agent.layouts/content.php on line 61
2017-04-05 12:33:48
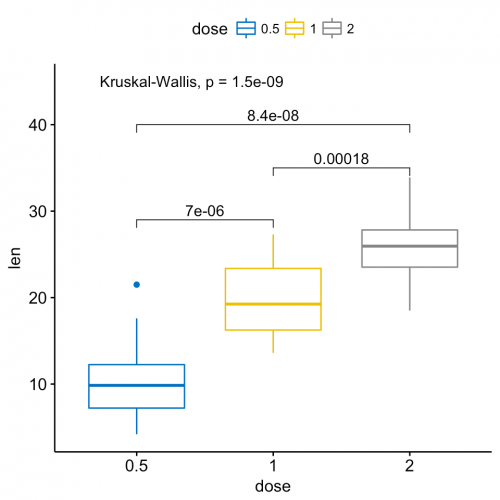
También hay una extensión del paquete ggsignif llamado ggpubr que es más potente cuando se trata de comparaciones multigrupo. Se basa en ggsignif, pero también maneja anova y kruskal-wallis, así como comparaciones de pares contra la media gobal.
Ejemplo:
ggboxplot(ToothGrowth, x = "dose", y = "len",
color = "dose", palette = "jco")+
stat_compare_means(comparisons = my_comparisons, label.y = c(29, 35, 40))+
stat_compare_means(label.y = 45)
Warning: date(): Invalid date.timezone value 'Europe/Kyiv', we selected the timezone 'UTC' for now. in /var/www/agent_stack/data/www/ajaxhispano.com/template/agent.layouts/content.php on line 61
2017-07-24 09:51:11
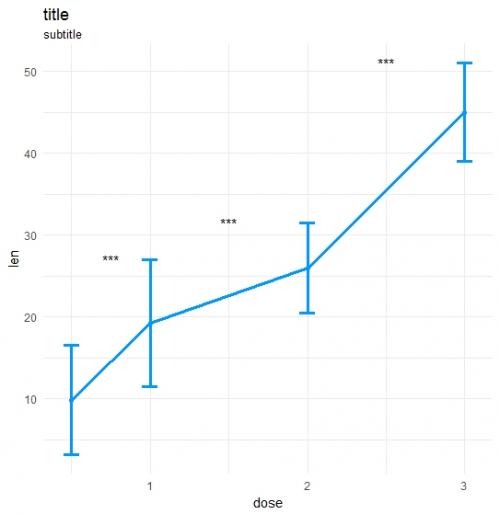
Hice mi propia función:
ts_test <- function(dataL,x,y,method="t.test",idCol=NULL,paired=F,label = "p.signif",p.adjust.method="none",alternative = c("two.sided", "less", "greater"),...) {
options(scipen = 999)
annoList <- list()
setDT(dataL)
if(paired) {
allSubs <- dataL[,.SD,.SDcols=idCol] %>% na.omit %>% unique
dataL <- dataL[,merge(.SD,allSubs,by=idCol,all=T),by=x] #idCol!!!
}
if(method =="t.test") {
dataA <- eval(parse(text=paste0(
"dataL[,.(",as.name(y),"=mean(get(y),na.rm=T),sd=sd(get(y),na.rm=T)),by=x] %>% setDF"
)))
res<-pairwise.t.test(x=dataL[[y]], g=dataL[[x]], p.adjust.method = p.adjust.method,
pool.sd = !paired, paired = paired,
alternative = alternative, ...)
}
if(method =="wilcox.test") {
dataA <- eval(parse(text=paste0(
"dataL[,.(",as.name(y),"=median(get(y),na.rm=T),sd=IQR(get(y),na.rm=T,type=6)),by=x] %>% setDF"
)))
res<-pairwise.wilcox.test(x=dataL[[y]], g=dataL[[x]], p.adjust.method = p.adjust.method,
paired = paired, ...)
}
#Output the groups
res$p.value %>% dimnames %>% {paste(.[[2]],.[[1]],sep="_")} %>% cat("Groups ",.)
#Make annotations ready
annoList[["label"]] <- res$p.value %>% diag %>% round(5)
if(!is.null(label)) {
if(label == "p.signif"){
annoList[["label"]] %<>% cut(.,breaks = c(-0.1, 0.0001, 0.001, 0.01, 0.05, 1),
labels = c("****", "***", "**", "*", "ns")) %>% as.character
}
}
annoList[["x"]] <- dataA[[x]] %>% {diff(.)/2 + .[-length(.)]}
annoList[["y"]] <- {dataA[[y]] + dataA[["sd"]]} %>% {pmax(lag(.), .)} %>% na.omit
#Make plot
coli="#0099ff";sizei=1.3
p <-ggplot(dataA, aes(x=get(x), y=get(y))) +
geom_errorbar(aes(ymin=len-sd, ymax=len+sd),width=.1,color=coli,size=sizei) +
geom_line(color=coli,size=sizei) + geom_point(color=coli,size=sizei) +
scale_color_brewer(palette="Paired") + theme_minimal() +
xlab(x) + ylab(y) + ggtitle("title","subtitle")
#Annotate significances
p <-p + annotate("text", x = annoList[["x"]], y = annoList[["y"]], label = annoList[["label"]])
return(p)
}
Datos y llamada:
library(ggplot2);library(data.table);library(magrittr);
df_long <- rbind(ToothGrowth[,-2],data.frame(len=40:50,dose=3.0))
df_long$ID <- data.table::rowid(df_long$dose)
ts_test(dataL=df_long,x="dose",y="len",idCol="ID",method="wilcox.test",paired=T)
Resultado:
Warning: date(): Invalid date.timezone value 'Europe/Kyiv', we selected the timezone 'UTC' for now. in /var/www/agent_stack/data/www/ajaxhispano.com/template/agent.layouts/content.php on line 61
2018-02-28 11:20:07